
オミクロン株は今までにない30個もの変異を持つ株で、これまでのワクチンや抗体が効かない可能性があると新聞に出ていた。人はウイルスに感染すると抗体ができて、新たにウイルスが体に入ってくると、異物と認識して抗体がウイルスを攻撃する。
現在のRNA-ワクチンは、注射されるとウイルスのスパイクを体の中で大量生産する。そこで体はそのスパイクを異物と認識できるようになる。
抗体カクテル療法は、何種類かの抗体を混ぜたもの処方することによって、ウイルスのスパイクが人に取り付く前にどれかの抗体がスパイクに結合させる。結果、人には結合できなくなる。
オミクロン株はこのスパイクの部分が変異してしまったので、体が異物として認識できなくなったのでは無いかと言われている。
それでは、そもそも、スパイクの部分はどのようなモノと強く結合するのだろうか?
ネットを検索していたところ、次の論文が見つかった。
Identification of Dietary Molecules as Therapeutic Agents to Combat COVID-19 Using Molecular Docking Studies
表では見にくいのでエクセルなどにコピペして見て欲しいのだが、食品やハーブ類に含まれる化合物とウイルス・スパイクの分子ドッキング・エネルギーが計算されている。
最も強くスパイクと結合しているのは、お茶の成分エピガロカテキンガレート(EGCG)であると言っている。
この論文は査読前の論文だし、そもそも、結合エネルギーと言っても計算機科学の産物なので、全てを真に受けるのは危険である。とは言え、化合物の構造が与えられていて、その結合エネルギーが与えられているなら解析しない手はない。
Smilesの構造式からHSPiPソフトウエアーのY-MB機能を使って熱力学的な物性値を計算する。HSPiPに搭載されているRDKitでトポロジカルな物性値を計算する。ついでにRDKitで3次元構造を生成させて、分子を取り巻く最小の立方体を計算する。
まず分子の最も長い長軸を探す。その長軸をZ軸に置き各原子をXY平面に投影し、一番長いものをY軸、そして厚みをX軸として最小の立方体を得る。
Drag=回転, Drag+Shift キー=拡大、縮小, Drag+コマンドキーかAltキー=移動。
そして、HSP、立方体、RDKitのKappa1-3を使ってQSAR式を作成する。
非線形解析ツール、MIRAIを使う。
自分で解析して見たい人用に私の使ったデータを載せておこう。最後の3つの化合物は予測用のデータになる。
データ数は18に対して、説明変数は17ある。
通常の重回帰法を使って解析するつもりなら、最後の化合物の予測値が幾つになるか結果を見て判断してみよう。
MIRAIで絶対誤差を最小にする方法で計算すると、結果は次のようになった。
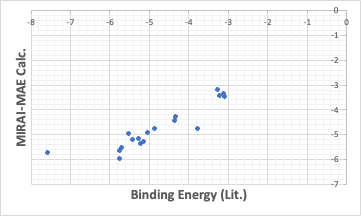
大きく外れるものが2-3あるが、他のものは直線上によく乗っている。MAEを指定すると、このように外れるものは更に大きく外れるようなQSAR式になる。
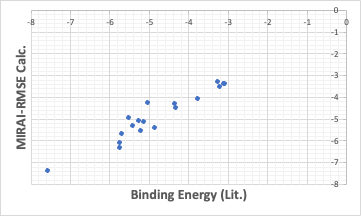
MIRAIで2乗誤差を最小にするアルゴリズムで計算すると、なるべく全てを直線の周りに配置したQSAR式になる。
これらの場合の結合エネルギーは、値が小さいほど強くなる。その観点からはMIRAI-RMSEの方が良いかもしれない。
しかし、非線形性があって、データ数が少なくて、説明変数が大量にある場合には、私なら、可能性を限定せずに、数種類の式の結果を見て、総合的に判断する。
ともかく、一旦こうした式が作成できれば、後はデータベースの中の数万化合物を計算して、HSP、立方体、RDKitのKappa1-3を取り出す。
そしてソートをかけて効果の高いものを取り出すだけなので、30分仕事で全て完了する。
仮定としてはドッキング計算がそこそこ正しいという前提には立っている。
しかし、数万化合物のドッキング計算を行なって候補を取り出すのがいいか、自分のようにMac miniで1時間で全てをこなすのが良いか、考えてみよう。
余った時間を他の有意義な事に使う方が、よほど豊かな人生になる。
デジタルで化学の豊かさを求めるpirikaならではのDXと言える。

「コロナウイルス、スパイクの結合エネルギーを予測してみよう」への3件のフィードバック