2026.3.31
pirika.comで化学
>チャピエモン-3rd Pirika Origin (CPO)
> ハンセン溶解度パラメータ (HSP)
> 化学全般
> 情報化学 >物性化学 >高分子化学 >化学工学 >その他の化学 >昔のもの
>情報化学ツール >MAGICIAN養成講座 >STEAM
>Pirika ツール群
ブログ
業務案内
お問い合わせ
情報化学ツール > 原子団寄与法>
原子団寄与法の基礎
Dynamic Group Contribution > DGC用のYMB4DGC
DGCの原子団拡張
DGCの応用例
[1. 概要]
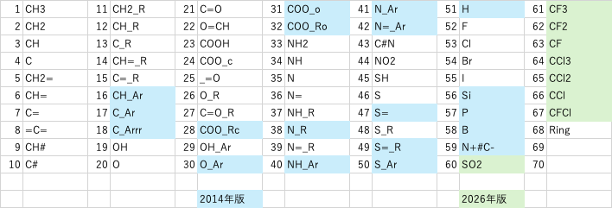
Pirika Proに搭載されているYMB[*1]はSMILES[*2]の構造式から原子団を認識する[*3]。その際に原子団同士の結合情報を残すように設計してある。原子団を全て認識させ終わった後に、結合情報をもとに原子団のアサインを変更することがある。例えば水酸基(OH)がCH2に結合している場合にはOHは1級である。芳香族に接続している時にはフェノール性のOHとして認識する。HSPiPやPirika Proに搭載のフルセットのYMBは172原子団を認識する。DGC用にはサブセットのYMBを使う(2026バージョンでは67原子団)。
[2. DGC結合テーブル作成用のYMBプログラム]
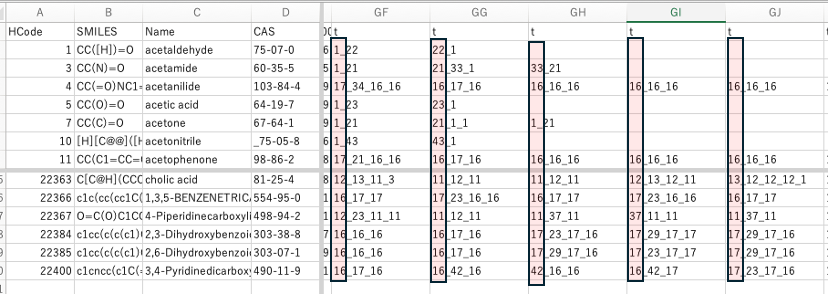
DGC用のデータフォーマットはメインの原子団にどんな原子団が付加しているのかのテーブルになる。メインの原子団に何個の原子団が付加するかはメイン原子団の手の数で決まる。大事なのは非対称の原子団の認識である。例えばエステル(COO)基は炭素の側につく原子団と酸素の側につく原子団は分けてテーブル化する。-C=のように2重結合と単結合の非対称原子団の場合にも、2重結合には2重結合が付加するという制限がある。2014年に拡張したあと2026年にSO2とフッ素、塩素原子団の拡張を行った。2026年度版の原子団のリストを表1に示す。YMB4DGCを使うとSmilesの構造式から結合テーブル(BT)を作る。メイン原子団と_を介して結合している原子団を記載する。結合している原子団が複数ある場合には、大きい原子団番号順に_で結合する。BTの一部を表2に示す。物性値とBTリストのテーブルができたら、DGCプログラムに入力して計算を行う[*4]
[3. 図表]
[X. Pirikaへのリンク]
*1: YMB Yamamoto Molecular Break 山本の作った分子の分割アルゴリズム
*2: Smiles線形表記法について (HSPiP Docs) Smilesの分子構造式 (MOOC)
*3: 官能基のリスト (TCPE), HSPiPで使える官能基一覧 (HSP/Docs)
*4: DGCの実際の使い方
Copyright pirika.com since 1999-
Mail: yamahiroXpirika.com (Xを@に置き換えてください)
メールの件名は[pirika]で始めてください。
